VIRUS A DNA
description
Transcript of VIRUS A DNA

1
VIRUS A DNA
Replicazione nucleare e citoplasmaticaHEPADNAVIRUS
Replicazione nucleare
Replicazione citoplasmatica POXVIRUS
.a DNAds = Adenovirus e Herpesvirus. Poxvirus.b DNAss = Parvovirus
1) DNA lineare
2) DNAds circolare = Hepadnavirus, Poliomavirus e Papillomavirus

2
Parvovirus - Papillomavirus e Poliomavirus: DNA pol cellulare
Adenovirus - Herpesvirus: DNA pol virale
> velocità> errori
Target per agenti antivirali(es. acyclovir, AZT)
REPLICAZIONE del DNA VIRALE
SEMICONSERVATIVA

3
REPLICAZIONE DEI VIRUS a DNA
PROBLEMI Richiesta di un primer di inizio della replicazione del DNA
lo stesso problema della cellula ospite: le DNA polimerasi non sono in grado di replicare il DNA a partire da uno stampo a ssDNA. Possono solo iniziare la replicazione a partire da regioni ds (5’ 3’)
•come replicare le estremità senza perdere informazione?•soluzione: specifiche caratteristiche strutturali dei genomi

4
Le sequenze Ori
From Flint et al. Principles of Virology (2000), ASM Press
siti di legame per proteine (Ori recognition proteins): Palindromi
sequenze ricche di AT: facilitano lo srotolamentote
sequenze dentro o vicino a regioni di controllo trascrizionale
siti di legame per fattori trascrizionali e proteine con funzione di enhancer , virali e/o cellulari (aumento dell’efficienza di replicazione)

5
Replicazione del genoma dei virus a DNA : le proteine di riconoscimento della regione ORI
From Flint et al. Principles of Virology (2000), ASM Press
Tutti i virus a DNA devono codificare almeno una proteina per iniziare la replicazione del genoma
legame di specifiche proteine alla regione ORI del genoma virale.il legame con le proteine tende a distorcere la regione ORI
eventuale reclutamento di proteine cellulari per la replicazione del DNA virale
Molte delle proteine reclutate sulla regione ORI hanno attività di elicasi ATP-dipendente per lo srotolamento del DNA virale
Caratteristiche comuni:
I virus più grandi codificano anche la loro DNA polimerasi e altre proteine essenziali per la replicazione del genoma

6
TRASCRIZIONE DEI VIRUS A DNA
Presenza di proteine regolatrici virali e/o cellulari che interagiscono con sequenze “promoter”al 5’ dei geni virali
5’ sequenze “cap”3’ poli A (100-200 residui di adenina)
Trascrizione di geni su filamenti diversi di DNA ed in direzione opposta (es. SV40 = early e late su filamenti opposti)
mRNA con introni Splicing
mRNA policistronicilettura in ORF differenti
Utilizzano RNA pol II cellulare

7
TRASCRIZIONE DEI VIRUS A DNA nel nucleo della cellula ospite
Replicazione del DNA
ecc: Poxvirus: Utilizzano enzimi presenti nel core del virione Trascritti senza introni. Assenza di splicing
- Organizzazione temporale (in 2 tempi) con:
mRNA precoci Proteine non-strutturali
mRNA tardivi Proteine strutturali

8
TRASCRIZIONE DEI VIRUS A DNA
- Organizzazione temporale (in 3 tempi) con:
immediati precoci (CHX insensibili)
Precoci ritardati (CHX sensibili)
Es. HERPESVIRUS
Replicazione del DNA
mRNA precoci
mRNA tardivi Proteine strutturali

9
DNA ds circolare (5.2 kbp)legato a istoni cellulari (H2A, H2B, H3 e H4)
Capside icosaedrico nudoVP1, VP2 e VP3
geni precoci replicazione DNA geni tardivi
Espressione temporale
mRNA E e L trascritti in modo divergente a partire da ORI
(45 nm)

10
tardive: proteine strutturali (VP1, VP2, VP3)
- regolano la loro stessa sintesi transizione della trascrizione da precoce a tardiva- attivano l’espressione dei geni tardivi
QuickTime™ and aGIF decompressor
are needed to see this picture.
- essenziale per la replicazione del DNA virale
interazione con pRB e p53 (induzione della fase S nella cellula ospite ed inibizione dell’apoptosi cellulare
Proteine di SV40
precoci: proteine T e t ( regolatorie e multifunzionali)

11
Replicazione del Genoma di SV40
sito di origine della replicazione (ORI)
la replicazione del DNA è bidirezionale (replicazione a Theta)
ORI = sequenza unica
Terminazione della sintesi del DNA a 180o da ORI ( congiunzione delle forche di replicazione)
2 esameri di proteina T legano un sito (sito II) della ORI
proteina T (elicasi) insieme a RpA cellulare (proteina di legame ssDNA) srotolano il DNA in modo da permettere la sintesi bidirezionale del DNA

12
QuickTime™ and aGIF decompressor
are needed to see this picture.
DNA ds circolare (8 kbp)legato a istoni cellulari
Capside icosaedrico nudo (L1,L2)
Specie-specificiTropismo per cellule dell’epitelio squamosoInfezione produttiva solo in cellule epiteliali differenziate
>100 tipi di HPV (Human Papilloma Virus) alto rischio: HPV-16, HPV-18, HPV-31, HPV-45
(55 nm)

13
PAPILLOMAVIRUS
7 geni E 2 geni L ( L1 e L2 strutturali)
E6 si lega a p53 : segnale per ubiquitina e degradazione
QuickTime™ and aGIF decompressor
are needed to see this picture.
E7 attiva la proteina Rb

14
I PAPILLOMAVIRUS: il ciclo virale

15
Proteine Virali• E2: fattore regolatore della trascrizione e della replicazione del DNA
virale.
• E1: fattore importante per la replicazione del DNA virale, si lega all’origine di replicazione posto nel LCR
• E4: e’ espressa come gene late. Overlaps E2, ma ha un differente ORF. Viene sintetizzata contemporaneamente alla relicazione del DNA, prima della sintesi di L1 ed L2
• E5: è altamente idrofobica, associata a membrane cellulari. Sembra induca una down regulation del sistema MHC
• E6: oncogene virale, interagisce con p53
• E7: oncogene virale, interagisce con pRb

16
QuickTime™ and aPhoto - JPEG decompressor
are needed to see this picture.
Capside icosaedriconudo 60-90 nm
Circa 100 sierotipi umani Infezioni respiratorie ed enteriche
Congiuntiviti acute
infezioni latenti nel tessuto linfatico di tonsille, adenoidi e placche del Peyer
(alcuni tipi oncogeni per roditori neonati)
isolati da adenoidi umane - 1953

17
ADENOVIRUS Genoma:dsDNA lineare
ITR ITR
(30-35 Kbp)
ITR = Inverted Terminal Repeat
Terminal proteinP55
5’desossicitosina
QuickTime™ and aGIF decompressor
are needed to see this picture.
QuickTime™ and aGIF decompressor
are needed to see this picture.

18
Espressione del genoma
Geni precoci = E1a, E1b, E2a, E2b (DNA pol), E3, E4
Geni tardivi = L1, L2, L3, L4, L5 (proteine strutturali)
ADENOVIRUS

19From Flint et al. Principles of Virology (2000), ASM Press
3. l’elica di DNA dislocata forma un “panhandle” via gli “inverted terminal repeats”
4.associazione Pol-pre-TP e ……
1. la Polimerasi virale forma un legame fosfodiesterico tra dCMP e pre-TP
il legame di Nf-1 e Oct-1 alla sequenza core Ori facilita la formazione del complesso
2. il 3’OH di dCMP serve da innesco per la sintesi (in continuo) del filamento di DNA complementare
Ad ssDBP (E2), e Topoisomerasi
5. sintesi (in continuo) del filamento complementare
Adenovirus: replicazione del DNA lineare la PROTEINA TERMINALE funge da PRIMER

20
Sottofamiglia Genere Tipo
AlphaherpesvirinaeSimplexvirus
Herpes simplex virus tipo 1
Herpes simplex virus tipo 2
Varicellovirus Virus VaricellaZoster
Betaherpesvirinae
Cytomegalovirus Citomegalovirus
Roseolovirus
Herpesvirus umano 6
Herpesvirus umano 7
Gammaherpesvirinae Lymphocrypto-virus
EpsteinBarr virus
Rhadinoviruso del sarcoma
Herpesvirusumano 8
di Kaposi
Capside icosaedricocon involucro
150 nm

21
QuickTime™ and aGIF decompressor
are needed to see this picture.
QuickTime™ and aGIF decompressor
are needed to see this picture.
Sequenze Uniche = U (L e S)
Sequenze Ripetute = R (L e S), (T e I)
Genoma di HSV-1 DNAds lineare QuickTime™ e undecompressore TIFF (Non compresso)sono necessari per visualizzare quest'immagine.
(150 Kb)

22
Genoma del virus Herpes Simplex di Tipo 1
Il genoma lineare quando entra del nucleo della cellula ospite circolarizza per la presenza di sequenze presenti alle due estremità TR
Il genoma viene trascritto ad opera della RNA polimerasi II cellulare

23
HSV-1:REPLICAZIONE DEL GENOMA
proteine necessarie per la sintesi del DNA viraleORI binding protein (UL9)helicase/primase complex (UL5, UL8, UL52). DNA polymerase (UL30), DNA binding proteins (UL42, UL29, ICP8)

24
Modello di replicazione del DNA dei virus erpetici Cerchio rotante
From Flint et al. Principles of Virology (2000), ASM Press
1. taglio della molecola circolare : 3’-OH utilizzato come primer
2. la sintesi della nuova elica provoca la dislocazione dell’elica complementare
3 e 4. sintesi in continuo della forma circolare e sintesi discontinua sull’elica dislocata con formazione di concatameri di dsDNA
Il taglio del DNA (sequenza terminale
ripetuta a) congiuntamente al processo di incapsidamento del DNA genera i nuovi genomi virali lineari

25
CICLO DIREPLICAZIO
NE
cascata di espressione
genica
assemblaggio e maturazione

26QuickTime™ and aGIF decompressor
are needed to see this picture.
Capside icosaedriconon-rivestito
18-28 nm
Parvovirus autonomi Dependovirus o Virus adeno-associati (AAV)
: 1 molecola lineare DNAss 4.5 - 6 Kb

27
Adeno-associati
QuickTime™ e undecompressore TIFF (Non compresso)sono necessari per visualizzare quest'immagine.
Ad
Virus satelliti: Per replicare richiedono attiva replicazione cellulare o la co-infezione con un virus helper (adenovirus o herpesvirus)
AAV

28
PARVOVIRUS: DNA lineare ss (4.5 - 6 Kb)
Sequenze terminali palindromiche
Sequenze terminali
filamento codificante: filamento(-)
QuickTime™ and aGIF decompressorare needed to see this picture.115nt 115nt

29
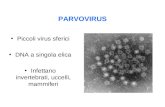
PARVOVIRUS
Per vedere questa immagineoccorre QuickTime™ e un
decompressore Photo - JPEG.
Regioni separate per:proteine non strutturali (gene NS1, gene rep) proteine strutturali (geni cap)

30
REPLICAZIONE DEL GENOMA DEI PARVOVIRUSrolling hairpin model
REP78 reazione nicking necessaria per la risoluzione dei terminali.
attività di elicasi essenziale per srotolamento della regione ITR
+













![buttazzo.ppt [modalità compatibilità] - Scuola Superiore ... · Robotica: programmazione di robot Genetica: (DNA = programma genetico) progettazione di cellule, batteri, virus ...](https://static.fdocumenti.com/doc/165x107/5c66319d09d3f2d12a8beb32/modalita-compatibilita-scuola-superiore-robotica-programmazione-di.jpg)




