Sequenziamento del DNA con metodica Sanger di genetica medica Specializzazioni... · Arricchimento...
Transcript of Sequenziamento del DNA con metodica Sanger di genetica medica Specializzazioni... · Arricchimento...

Sequenziamento del DNA con metodica Sanger



1a generazionesequenziamento del DNA secondo il metodo
Sanger
Il sequenziamento automatico secondo il metodo Sangerha dominato nella scienza e nell’industria per almeno 20 anni e ha consentito il sequenziamento del genoma umano e la scoperta di oltre 2.500 malattie genetiche monogeniche
Il metodo Sanger è considerato la tecnologia di “prima generazione”, mentre i nuovi metodi sono denominati “next-generation sequencing (NGS)”

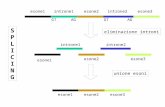
Sanger DNA sequencing

2a generazione“next-generation sequencing (NGS)”
Il principale vantaggio è la possibilità tecnica di produrre un volume enorme di dati a costi estremamente più bassi ed in tempi estremamente più rapidi
Il potenziale dell’NGS è simile ai primi tempi della PCR con il limite principale dovuto all’immaginazione

NGS

Preparazione del DNA da sequenziare
Una comune strategia tecnologie NGS è che il template è adeso o immobilizzato su una superficie solida o supportoL'immobilizzazione di molecole spazialmente separate permette di eseguite simultaneamente migliaia o milioni di reazioni di sequenziamento

Come si prepara il DNA?
Tecniche basate sull’amplificazione:1. emulsion PCR (emPCR) (454, Life)2. solid-phase amplification (Solexa)
Tecniche non basate sull’amplificazione:1. immobilizzazione dei primer (Helicos)2. immobilizzazione del “template” (Helicos)3. immobilizzazione dell’enzima (Pacific, LI-COR)

emulsion PCR (emPCR)

emulsion PCR (emPCR)


Il 5500xl SOLiD legge 200.000.000.000 di basi/corsa

Solid-phase amplification can produce 100–200 million spatially separated template clusters (Illumina/Solexa)

I gruppi bloccanti attaccati al 3’causano un ostacolo nell’incorporazione di un altro nucleotide, ma l’ostacolo può essere rimosso

L’Illumina HiSeq2000 legge oltre 600.000.000.000 di basi di DNA per corsa

A doubling of sequencing output every 9 months has outpaced and overtaken performance improvements within the disk storage and high-performance
computation fields
S D Kahn Science 2011;331:728-729

• Whole Genome Seq• Exome Seq• RNA Seq• MeDIP Seq• miRNA Seq• Epigenetics, DNA methylation, ChIP-Seq• Copy Number Variation• Gut Bacteria / Metagenome• Skin Bacteria / Metagenome• Infectious Diseases• NGS Applications in Cancer• Biomarkers• Stem Cells• Detection of Genome Structural Variation• Personalised Medicine Applications

The term NGS defines very different sizes of analysis!
• Whole genome @40 x (~ 140 Gb of sequences/sample) √
• Whole exome @60 x (~ 5 Gb/sample) √ √
• A set of 100 aver. candidate genes(exons) @100 x (~ 0.1 Gb/sample) √ √ √
• A single medium-size gene (exons and introns) @100x (~ 0.005 Gb/sample) √

The genome of James Watson
7.4 x coverage
234 runs
24.5 billions bp

11 genetic diseases !!

Whole Genome Seq

very heterogeneous genotype, genetic testing for 15/39 loci


Pedigree of the family and segregation of SH3TC2 mutations

Arricchimento “enrichment”• Tutti i geni (esoni+introni) di una regione cromosomica dove è mappata una malattia genetica da causa ignota
• Tutti gli esoni di tutti i geni coinvolti in varie forme di quella malattia genetica
• Tutti gli esoni di tutti i geni noti del genoma umano (esoma umano)
Meno dell’1% delle mutazioni che causano malattie genetiche cadono fuori dagli esoni

The RNA is transcribed from PCR-amplified oligodeoxynucleotides originally synthesized on a microarray, generating sufficient bait for multiple captures at concentrations high enough to drive the hybridization





minigenome preparation


Come si fa a comprendere quale variazione nella sequenza del DNA possa avere un significato patologico?